当一位科研人员被RNA-seq数据分析、化合物结构预测、临床报告撰写等重复劳动占据大量时间时,OpenClaw的153个科学计算Skill全家桶给出了颠覆性解决方案——这些Skill并非简单插件,而是将生物信息、化学药物、临床医学、数据科学等领域的专业知识与工具封装成的“科研超能力”。只需一句自然语言指令,AI就能调用对应Skill,完成从数据质控、分析建模到论文写作、图表生成的全流程操作,让科研人员从机械劳动中解放,专注核心创意与科学发现。
本文将完整拆解2026年OpenClaw的阿里云(零基础速通)与本地部署步骤,深度解析153个科研Skill的分类价值、核心功能与实战用法,包含可直接复制的安装命令与场景化指令示例,助力科研人员快速搭建专属AI实验室,实现科研效率质的飞跃。阿里云上OpenClaw极速一键部署最简单,步骤详情 访问阿里云OpenClaw一键部署专题页面 了解。

一、核心认知:科研Skill的本质——知识封装的科研超能力
(一)为什么科研Skill能颠覆传统科研模式?
传统科研流程中,一个简单的RNA-seq数据分析需要科研人员掌握Python编程、生信工具使用、统计建模等多项技能,耗时数天甚至数周;而OpenClaw的科研Skill通过“专业知识+工具链+流程标准化”的封装,实现了三大突破:
- 门槛归零:无需编程基础、无需记忆复杂命令,仅用自然语言指令即可触发专业分析流程,新手也能快速上手;
- 效率倍增:将原本需要数天的分析任务压缩至分钟级,例如单细胞RNA-seq分析全流程仅需5分钟,论文图文摘要生成仅需3分钟;
- 质量可控:Skill内置领域标准流程与期刊规范(如Nature图表格式、IMRAD论文结构),输出结果直接满足投稿要求,避免反复修改。
(二)153个科研Skill分类全景(核心价值解析)
OpenClaw的科学计算Skill覆盖9大核心领域,每个Skill都是对应领域的“屠龙刀”,精准解决科研痛点:
| 领域分类 | Skill数量 | 核心功能 | 代表Skill | 适用场景 |
|---|---|---|---|---|
| 生物信息 | 15个 | 序列处理、单细胞分析、差异表达、数据库查询 | biopython、scanpy、pydeseq2、kegg-database | RNA-seq数据分析、蛋白质结构预测、代谢通路分析 |
| 化学/药物 | 10个 | 分子处理、药物发现、化合物数据库查询 | rdkit、deepchem、drugbank-database、pubchem-database | 药物分子设计、化合物筛选、化学结构生成 |
| 临床医学 | 5个 | 临床决策、报告生成、临床试验查询 | clinical-decision-support、pyhealth、clinicaltrials-database | 临床数据处理、治疗方案制定、临床试验检索 |
| 数据科学 | 29个 | 数据处理、机器学习、统计建模、强化学习 | scikit-learn、pandas、pymc、stable-baselines3 | 科研数据清洗、建模分析、预测推理 |
| 可视化 | 8个 | 学术图表、幻灯片、海报生成 | matplotlib、plotly、scientific-visualization、latex-posters | 论文图表绘制、学术海报制作、报告可视化 |
| 文献/写作 | 9个 | 论文写作、文献综述、引用管理 | scientific-writing、literature-review、pubmed-database | 科研论文撰写、文献检索汇总、参考文献格式化 |
| 实验/实验室 | 9个 | 实验自动化、电子实验记录、机器人控制 | opentrons-integration、benchling-integration、pylabrobot | 液体处理机器人操作、实验流程自动化、电子实验记录本同步 |
| 数据库 | 2个 | 组学数据管理、VCF数据存储 | lamindb、tiledbvcf | 大规模组学数据管理、基因数据存储 |
| 其他 | 66个 | 量子计算、天文学、地理信息、深度学习 | qiskit、astropy、geopandas、transformers | 跨学科科研场景、前沿技术研究 |
(三)四大王牌Skill深度解析(科研必备)
1. scientific-writing(论文写作神器)
- 核心价值:按学术规范自动生成论文,无需手动调整格式,直接满足期刊要求;
- 关键特性:
- 强制IMRAD结构(引言→方法→结果→讨论),拒绝碎片化表达;
- 遵循CONSORT/STROBE/PRISMA等报告规范,适配不同学科投稿;
- 自动生成图文摘要(Graphical Abstract),提升论文传播力;
- 实战指令:“用scientific-writing技能,基于RNA-seq差异表达分析结果,撰写一篇符合Nature子刊要求的论文引言与结果部分,包含3个核心发现,引用5篇相关文献”。
2. scientific-visualization(出版级图表工具)
- 核心价值:生成符合顶级期刊标准的图表,无需手动调整格式与配色;
- 关键特性:
- 适配期刊要求:Nature单栏3.5英寸、双栏7英寸宽度,Science色盲友好配色;
- 精准标注:自动添加误差线、显著性标记(p<0.05, *p<0.01);
- 高清输出:支持PDF/EPS/TIFF格式,300-600 DPI,满足印刷要求;
- 实战指令:“用scientific-visualization技能,将差异表达基因数据生成火山图与热图,按Cell期刊格式,配色采用色盲友好方案,输出TIFF格式”。
3. opentrons-integration(实验室机器人控制)
- 核心价值:AI直接控制液体处理机器人,实现实验自动化,无需人工操作;
- 关键特性:
- 支持96孔板/384孔板操作,自动完成加样、稀释、混合等步骤;
- 适配Opentrons主流机器人型号,无需复杂编程;
- 实验流程可视化,可实时监控执行进度;
- 实战指令:“用opentrons-integration技能,控制Opentrons OT-2机器人,完成96孔板的RNA提取前处理,按每孔50μL样本+100μL裂解液的比例混合,室温静置10分钟”。
4. paper-2-web(论文多媒体转化)
- 核心价值:将单一论文转化为多形态传播载体,提升学术影响力;
- 关键特性:
- 支持转化为交互式网页、视频解说、学术海报三种形态;
- 网页自动添加数据可视化组件,支持读者交互探索;
- 视频解说自动生成配音与字幕,适配学术会议展示;
- 实战指令:“用paper-2-web技能,将这篇单细胞RNA-seq分析论文转化为交互式网页与学术海报,网页包含UMAP交互图,海报采用A0尺寸,适配国际会议展示”。
二、2026年OpenClaw双部署流程(新手零基础友好)
部署是使用科研Skill的基础,以下提供阿里云(长期稳定运行、大规模数据处理)与本地(隐私优先、离线使用)两种方案,新手可按需选择,全程复制粘贴命令即可完成。
方案一:阿里云部署(大规模科研计算首选)
阿里云部署依托弹性计算资源,支持153个Skill同时运行,适合处理大规模组学数据、长时间模拟计算等场景,无需担心本地硬件配置不足,新手5分钟即可完成部署。
(一)部署前置准备
- 阿里云账号:注册并登录阿里云账号,完成实名认证(个人用户支付宝刷脸即时生效),确保账号无欠费;
- 核心凭证:阿里云百炼API-Key(访问订阅阿里云百炼Coding Plan,用于调用大模型),获取路径:登录阿里云百炼控制台→密钥管理→创建API-Key,生成后立即复制保存(仅显示一次);
- 辅助工具:Chrome/Edge浏览器(访问阿里云控制台)、SSH工具(FinalShell,可选)。
新手零基础阿里云上部署OpenClaw喂饭级步骤流程
第一步:访问打开阿里云OpenClaw一键部署专题页面,找到并点击【一键购买并部署】。


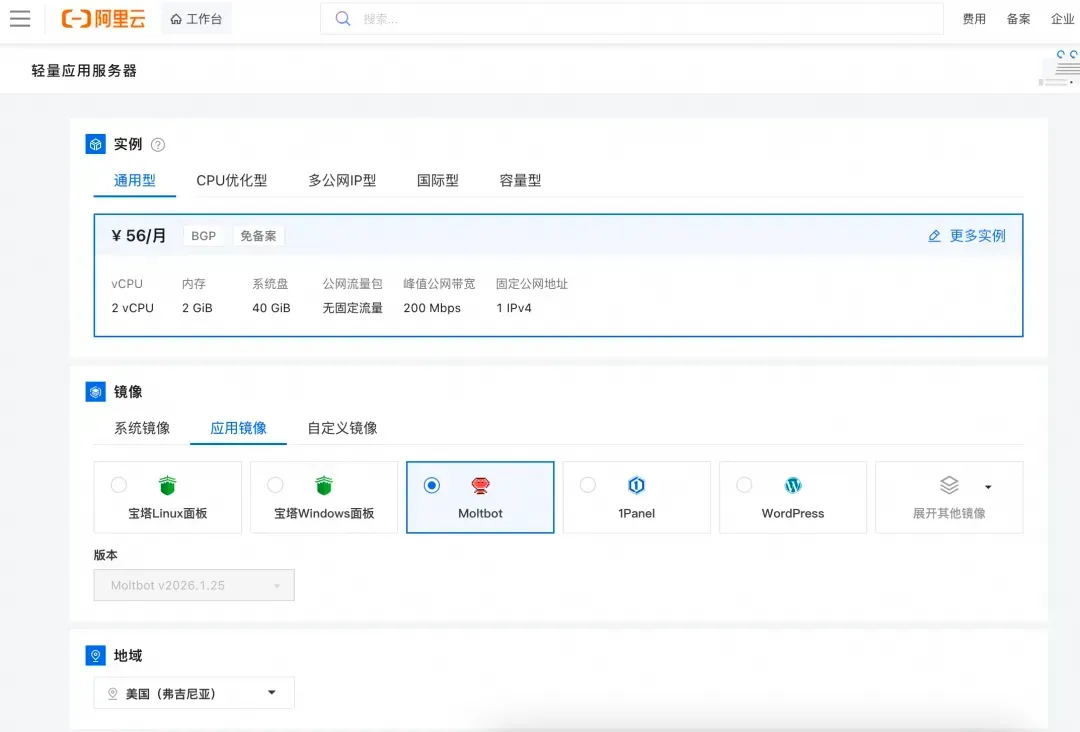
第二步:选购阿里云轻量应用服务器,配置参考如下:
- 镜像:OpenClaw(Moltbot)镜像(已经购买服务器的用户可以重置系统重新选择镜像)
- 实例:内存必须2GiB及以上。
- 地域:默认美国(弗吉尼亚),目前中国内地域(除香港)的轻量应用服务器,联网搜索功能受限。
- 时长:根据自己的需求及预算选择。

第三步:访问阿里云百炼大模型控制台,找到密钥管理,单击创建API-Key。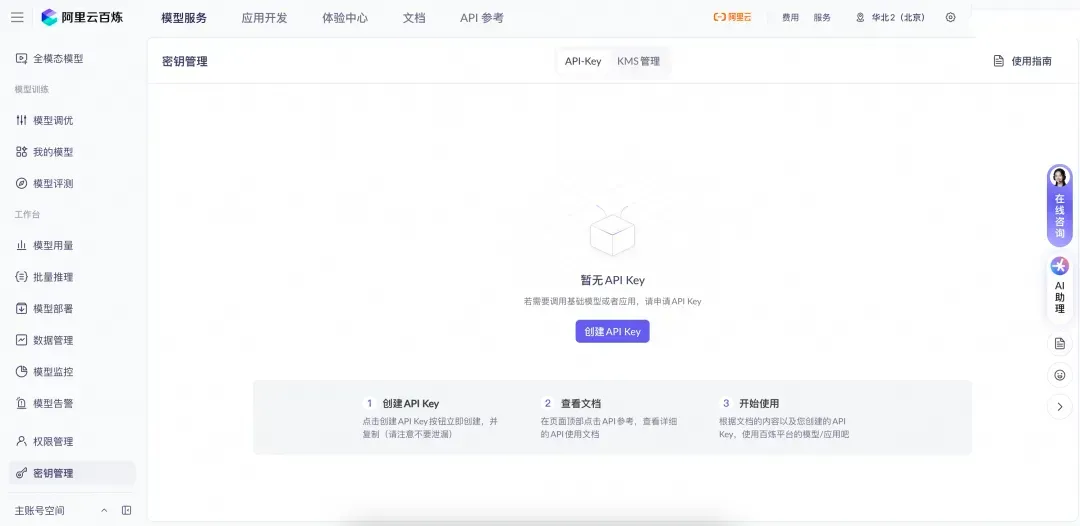
前往轻量应用服务器控制台,找到安装好OpenClaw的实例,进入「应用详情」放行18789端口、配置百炼API-Key、执行命令,生成访问OpenClaw的Token。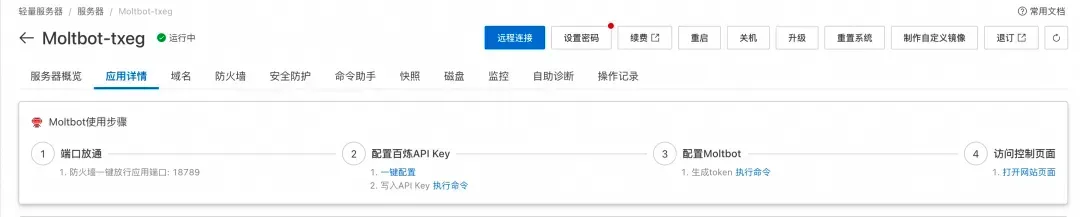
- 端口放通:需要放通对应端口的防火墙,单击一键放通即可。
- 配置百炼API-Key,单击一键配置,输入百炼的API-Key。单击执行命令,写入API-Key。
- 配置OpenClaw:单击执行命令,生成访问OpenClaw的Token。
- 访问控制页面:单击打开网站页面可进入OpenClaw对话页面。
(二)三步极速部署流程
第一步:购买服务器并部署OpenClaw镜像
- 访问阿里云OpenClaw一键部署专题页面,点击【一键购买并部署】,跳转至服务器配置页面;
- 核心配置选择(科研场景推荐):
- 镜像:默认选中“OpenClaw 2026科研版”应用镜像,预置Python科学计算库、生物信息工具等所有依赖;
- 实例规格:推荐4vCPU+8GiB内存+100GiB ESSD+200Mbps带宽(支持单细胞数据、药物分子模拟等大规模计算);
- 地域:优先选择中国香港/美国(弗吉尼亚),免ICP备案,支持海外数据库无限制访问;
- 购买时长:短期项目选月付,长期科研选年付(新手专享低成本套餐);
- 提交订单并完成支付,等待1-3分钟,直至服务器实例状态变为“运行中”,记录“公网IP地址”。
第二步:配置端口与API-Key
- 端口放行:进入服务器实例详情页→防火墙→点击“一键放通”,自动放行18789端口(OpenClaw核心通信端口)与8080端口(数据可视化端口);
- 配置大模型密钥:进入实例详情页→应用详情→“配置阿里云百炼API”模块,粘贴API-Key,点击“执行命令”,系统自动重启服务;
- 生成访问Token:在“应用详情”页面找到“Token配置”模块,点击“执行命令”,生成唯一Token(格式:token: xxxxxxxx-xxxx-xxxx-xxxx-xxxxxxxxxxxx),复制保存(严禁泄露)。
第三步:验证部署与科研环境
- 访问Web控制台:浏览器输入
http://服务器公网IP:18789/?token=你的Token,进入OpenClaw对话界面; - 科研环境验证:发送指令“测试scientific-visualization技能,生成一个简单的散点图”,AI能正常生成图表即为部署成功;
- 补充依赖安装(科研场景必备):
# 安装生物信息核心依赖(阿里云部署) sudo apt install -y samtools bedtools hisat2 star featurecounts # 安装Python科学计算库 pip3 install biopython scanpy scvi-tools pydeseq2 rdkit deepchem --index-url=https://pypi.tuna.tsinghua.edu.cn/simple
- 访问Web控制台:浏览器输入
方案二:本地部署(Windows/Mac,隐私优先首选)
本地部署所有数据存储在本地设备,适合处理敏感科研数据(如临床数据、未发表的实验结果),支持离线使用,Windows 10+/MacOS 12+系统均兼容。
(一)Windows系统本地部署
基础环境准备:
- 安装Git:访问Git官网,下载Windows版本,默认配置安装;
- 安装Node.js:访问Node.js官网,下载Windows 64位安装包,勾选“Add to PATH”,默认安装;
- 安装Python:访问Python官网,下载3.9+版本,勾选“Add Python.exe to PATH”,默认安装;
- 安装科研核心依赖:管理员模式PowerShell执行:
# 安装生物信息工具(需提前安装WSL2) wsl --install wsl sudo apt update && sudo apt install -y samtools bedtools hisat2 # 安装Python科学计算库 pip install biopython scanpy scvi-tools pydeseq2 rdkit deepchem pandas matplotlib plotly --index-url=https://pypi.tuna.tsinghua.edu.cn/simple - 验证环境:
git --version node --version # 需≥v18.0.0 python --version # 需≥3.9.0 pip list | grep scanpy
安装OpenClaw主程序:
# 克隆OpenClaw 2026科研版仓库 git clone https://github.com/openclaw/openclaw.git cd openclaw # 创建Python虚拟环境并激活 python -m venv venv .\venv\Scripts\Activate.ps1 # 安装依赖 pip install -r requirements.txt --index-url=https://pypi.tuna.tsinghua.edu.cn/simple npm install --registry=https://registry.npmmirror.com # 初始化配置(按提示输入阿里云百炼API-Key) npm run onboard启动服务与验证:
# 启动OpenClaw服务 npm run start # 生成访问Token openclaw token generate # 访问Web控制台:浏览器输入http://localhost:18789/?token=生成的Token # 测试科研Skill openclaw run --command "用biopython技能,读取FASTA文件格式,提取前10条序列的ID与长度"
(二)Mac系统本地部署
基础环境准备:
# 安装Homebrew(若未安装) /bin/bash -c "$(curl -fsSL https://raw.githubusercontent.com/Homebrew/install/HEAD/install.sh)" # 安装核心依赖 brew install git node@22 python@3.9 samtools bedtools hisat2 brew link node@22 --force brew link python@3.9 --force # 安装Python科学计算库 pip3 install biopython scanpy scvi-tools pydeseq2 rdkit deepchem pandas matplotlib plotly --index-url=https://pypi.tuna.tsinghua.edu.cn/simple # 验证环境 git --version node --version python3 --version pip3 list | grep scanpy安装OpenClaw主程序:
git clone https://github.com/openclaw/openclaw.git cd openclaw python3 -m venv venv source venv/bin/activate pip3 install -r requirements.txt --index-url=https://pypi.tuna.tsinghua.edu.cn/simple npm install --registry=https://registry.npmmirror.com npm run onboard启动服务与验证:
# 后台启动服务 nohup npm run start > ~/.openclaw/logs/local-start.log 2>&1 & # 生成访问Token openclaw token generate # 访问Web控制台:浏览器输入http://localhost:18789/?token=生成的Token # 测试科研Skill openclaw run --command "用matplotlib技能,生成一个符合Nature格式的折线图,展示不同处理组的基因表达量变化"
(三)本地部署避坑要点
- Windows坑1:WSL2未安装导致生物信息工具安装失败
- 解决方案:执行
wsl --install安装WSL2,重启电脑后重新安装samtools等工具;
- 解决方案:执行
- Mac坑2:rdkit安装失败(依赖缺失)
- 解决方案:通过conda安装rdkit,执行
conda install -c conda-forge rdkit,再重新配置OpenClaw;
- 解决方案:通过conda安装rdkit,执行
- 通用坑3:Python依赖版本冲突
- 解决方案:使用虚拟环境隔离依赖,执行
python -m venv venv激活虚拟环境后,重新安装所有依赖;
- 解决方案:使用虚拟环境隔离依赖,执行
- 通用坑4:大规模数据处理时内存不足
- 解决方案:关闭其他占用内存的程序,或升级设备内存(推荐32GB以上用于单细胞数据处理)。
三、科研Skill实战:三大核心场景全流程演示
以下通过生物信息、化学药物、临床医学三大高频场景,演示OpenClaw科研Skill的实战用法,所有指令可直接复制发送至Web控制台,阿里云/本地部署通用。
场景1:RNA-seq数据分析全流程(生物信息场景)
- 数据准备:将RNA-seq原始数据(FASTQ文件)上传至工作目录(阿里云:
/root/workspace/;本地:~/workspace/); - 下达指令:
```
用OpenClaw的RNA-seq分析Skill组合完成全流程: - 用FastQC进行数据质控,过滤低质量 reads(Q30<80%的序列);
- 用STAR工具将clean reads比对到人类基因组(hg38);
- 用featureCounts进行基因表达定量;
- 用pydeseq2进行差异表达分析(分组:处理组vs对照组);
- 用scientific-visualization生成火山图、热图(按Cell期刊格式);
- 用kegg-database注释差异基因的代谢通路;
- 用scientific-writing撰写结果部分,包含3个核心发现。
``` - 执行结果:
- 输出质控报告、比对率统计、差异表达基因列表(CSV格式);
- 生成符合期刊要求的图表文件(TIFF格式);
- 自动撰写结构化结果段落,可直接用于论文投稿。
场景2:药物分子筛选与设计(化学/药物场景)
- 数据准备:提供目标靶点蛋白结构文件(PDB格式);
- 下达指令:
```
用化学/药物类Skill完成药物分子筛选: - 用pubchem-database搜索与目标靶点相关的100个化合物;
- 用rdkit计算化合物的物理化学性质(分子量、脂水分配系数、氢键供体/受体);
- 用deepchem构建分子对接模型,筛选出结合能最低的10个化合物;
- 用scientific-visualization生成化合物结构与靶点结合模式图(按Nature Chemical Biology格式);
- 用medchem技能评估化合物的成药性(Lipinski规则)。
``` - 执行结果:
- 输出化合物筛选结果表(包含结合能、成药性评分);
- 生成化合物结构与靶点对接示意图;
- 提供成药性评估报告,标记不符合规则的化合物及优化建议。
场景3:临床数据处理与报告生成(临床医学场景)
- 数据准备:上传临床病例数据(包含症状、检查指标、治疗方案);
- 下达指令:
```
用临床医学类Skill处理临床数据: - 用pyhealth技能构建临床结局预测模型,分析影响治疗效果的关键因素;
- 用clinicaltrials-database搜索相关疾病的最新临床试验进展;
- 用clinical-reports技能生成符合STROBE规范的临床报告,包含患者基线特征、治疗效果、不良反应;
- 用treatment-plans技能为相似病例制定个性化治疗方案。
``` - 执行结果:
- 输出临床预测模型结果(准确率、关键影响因素);
- 生成结构化临床报告,可直接用于病例讨论;
- 提供个性化治疗方案建议,包含药物选择、剂量调整、随访计划。
四、科研Skill管理与进阶配置
(一)核心Skill安装命令(科研场景必备)
# 1. 安装生物信息类核心Skill
openclaw skills install biopython scanpy pydeseq2 kegg-database uniprot-database
# 2. 安装化学/药物类核心Skill
openclaw skills install rdkit deepchem drugbank-database pubchem-database
# 3. 安装数据科学与可视化Skill
openclaw skills install scikit-learn pandas matplotlib plotly scientific-visualization
# 4. 安装论文写作与文献Skill
openclaw skills install scientific-writing literature-review pubmed-database citation-management
# 5. 安装实验自动化Skill
openclaw skills install opentrons-integration benchling-integration
# 6. 查看已安装科研Skill
openclaw skills list --category "生物信息"
openclaw skills list --category "化学/药物"
# 7. 更新所有科研Skill
openclaw skills update --all
(二)进阶配置:批量数据处理与定时任务
批量处理脚本:编写Shell脚本批量处理多个样本数据,例如:
# 创建批量RNA-seq分析脚本(保存为batch_rna_seq_analysis.sh) #!/bin/bash for sample in `ls /root/workspace/fastq/*.fastq.gz` do sample_name=$(basename $sample .fastq.gz) echo "开始处理样本:$sample_name" openclaw run --command "用RNA-seq分析Skill组合处理$sample,输出结果保存到/root/workspace/results/$sample_name" done # 执行脚本 chmod +x batch_rna_seq_analysis.sh ./batch_rna_seq_analysis.sh定时任务配置:设置定时任务自动运行实验或分析,例如:
# 配置每日凌晨2点自动运行实验数据质控 openclaw cron add \ --name "daily-data-qc" \ --schedule "0 2 * * *" \ --skill "fastqc,scanpy" \ --params '{"inputDir":"/root/workspace/fastq", "outputDir":"/root/workspace/qc-results"}' # 启动定时任务 openclaw cron start
(三)Skill扩展:自定义科研流程
若现有Skill无法满足特定需求,可自定义科研流程并封装为Skill,例如:
- 创建自定义Skill配置文件(custom-rna-seq.skill):
{ "name": "custom-rna-seq", "description": "自定义RNA-seq分析流程(适配植物基因组)", "steps": [ { "skill": "fastqc", "params": { "qualityThreshold": 30}}, { "skill": "hisat2", "params": { "genome": "arabidopsis-tair10"}}, { "skill": "featureCounts", "params": { "gtf": "/data/gtf/arabidopsis.gtf"}}, { "skill": "pydeseq2", "params": { "contrast": "treatment:control"}}, { "skill": "scientific-visualization", "params": { "journal": "Plant Cell"}} ] } - 安装自定义Skill:
openclaw skills install --file custom-rna-seq.skill - 调用自定义Skill:
用custom-rna-seq技能处理拟南芥RNA-seq数据,输入文件路径:/root/workspace/arabidopsis.fastq
五、常见问题排查(科研场景必看)
(一)Skill安装失败(依赖缺失)
- 原因:科研Skill依赖的生物信息工具(如samtools、STAR)或Python库(如rdkit、scanpy)未安装;
- 解决方案:
# 安装生物信息工具(Linux/Mac) sudo apt install -y samtools star hisat2 featurecounts # Linux brew install samtools star hisat2 featurecounts # Mac # 安装Python库(国内镜像加速) pip install rdkit scanpy scvi-tools --index-url=https://pypi.tuna.tsinghua.edu.cn/simple
(二)数据分析报错(数据格式错误)
- 原因:输入数据格式不符合Skill要求(如FASTQ文件格式错误、PDB文件缺失原子坐标);
- 解决方案:
- 用基础工具验证数据格式:
fastqc 样本.fastq.gz(验证FASTQ)、pdb-tools check 蛋白.pdb(验证PDB); - 发送指令让AI自动修复:“用biopython技能修复FASTQ文件格式错误,去除不合格序列”。
- 用基础工具验证数据格式:
(三)图表格式不符合期刊要求
- 原因:Skill默认配置与目标期刊要求不一致;
- 解决方案:
- 明确指定期刊参数:“用scientific-visualization技能重新生成热图,期刊为Science,单栏宽度,配色方案为Viridis,添加样本分组标签”;
- 手动调整配置文件:
修改期刊参数(如宽度、配色、分辨率),重启服务生效。# 编辑可视化Skill配置 nano ~/.openclaw/skills/scientific-visualization/config.json
(四)大规模数据处理卡顿
- 原因:服务器/本地设备内存、CPU资源不足;
- 解决方案:
- 阿里云部署:升级服务器实例规格(如4vCPU+8GiB→8vCPU+16GiB);
- 本地部署:关闭其他程序,使用Dask进行并行计算:
# 启用并行计算 openclaw config set skills.dask.enabled true openclaw config set skills.dask.workers 4 # 按CPU核心数设置
六、总结
OpenClaw的153个科研Skill全家桶,彻底重构了传统科研模式——将原本需要数月学习才能掌握的专业工具与流程,封装为一句自然语言指令即可调用的“超能力”。无论是生物信息分析、药物分子设计,还是临床数据处理、论文写作,都能通过Skill组合快速完成,让科研人员从重复劳动中解放,专注于科学创意与核心发现。
本文详细拆解了OpenClaw的双部署流程、153个科研Skill的分类价值、四大王牌Skill的核心功能与实战用法,所有代码命令可直接复制执行,新手零基础也能快速搭建专属AI实验室。阿里云部署适合大规模科研计算与长期运行,本地部署适合隐私敏感场景与离线使用,用户可按需选择。
需要注意的是,科研Skill是“工具赋能”而非“替代科研人员”——AI负责执行机械性、流程化的工作,而科研人员需把控研究方向、解读分析结果、提出创新假设。随着使用深入,你还可以自定义Skill封装专属科研流程,让AI更贴合自身研究需求。
未来,OpenClaw的科研Skill生态还将持续扩展,覆盖更多前沿学科与技术场景,推动科研效率的进一步提升。对于科研人员而言,掌握这一工具,无疑能在激烈的学术竞争中占据先机。

